|
Schönen guten Tag, ich bräuchte dringend Hilfe in LaTeX. Wenn mir jemand bitte helfen könnte, wäre es sehr toll! Könnte jemand von euch bitte Schritt 3 bis dort, wo Schritt 5 aufhört, in LaTeX für mich machen? Das wäre sehr toll, dann würde ich wahrscheinlich den Rest alleine hinbekommen. Allerdings bräuchte ich wirklich diese enorme Starthilfe und es wäre super, wenn mir jemand damit helfen würde (auch wenn es viel Arbeit ist). Schon mal vielen, vielen Dank im Voraus! |
|
Ich habe nicht wirklich Lust, das komplette Schema für Dich zu basteln, aber da Du Schritte 3 bis 5 explizit erwähnst, nehme ich an, Deine Probleme sind
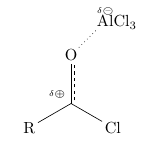
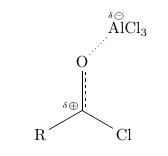
Die ersten zwei Punkte kann man mit TikZ erreichen. Für den zweiten Punkt verwendet man Für (nicht nur) formale Ladungen gibt es Ich werde Dir in einzelnen Beispielen verschiedene Bausteine der problematischen Stellen zeigen, und hoffe, dass sie Dir weiterhelfen. Die folgenden Beispiele haben alle diese Präambel: \documentclass{article} \usepackage{chemfig} \usetikzlibrary{decorations}% chemfig lädt TikZ % eine delokalisierte Doppelbindung \pgfdeclaredecoration{ddbond}{initial}{ \state{initial}[width=4pt]{ \pgfpathlineto{\pgfpoint{4pt}{0pt}} \pgfpathmoveto{\pgfpoint{2pt}{2pt}} \pgfpathlineto{\pgfpoint{4pt}{2pt}} \pgfpathmoveto{\pgfpoint{4pt}{0pt}} } \state{final}{\pgfpathlineto{\pgfpointdecoratedpathlast}} } \tikzset{ lddbond/.style={decorate,decoration=ddbond}, rddbond/.style={decorate,decoration={ddbond,mirror}}, elmove/.style={->,red,shorten >=3pt, shorten <=3pt} } \usepackage{chemmacros}% für formale Ladungen Hier ist ein Beispiel für Substanz 2:
\chemfig{ R-[:30]@{C}( -[:90,,,,rddbond]O -[:45,,,,dotted]@{Al}AlCl_3 )-[:-30]Cl } \chemmove{ \draw (C) node[above left] {\fdelp}; \draw (Al) node[above] {\fdelm}; } Alternativ (und wohl einfacher):
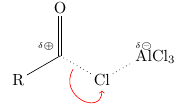
\chemfig{ R-[:30]( -[:90,,,,rddbond]O -[:45,,,,dotted]\chemabove{Al}{\fdelm}Cl_3 )(-[:160,.25,,,draw=none]\fdelp) -[:-30]Cl } Hier ein Beispiel für Schritt 3:
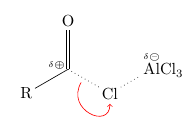
\chemfig{ R-[:30]@{C}( =[:90]O ) -[@{b}:-30,,,,dotted]@{Cl}Cl -[:30,,,,dotted]@{Al}AlCl_3 } \chemmove{ \draw (C) node[above left] {\fdelp}; \draw[elmove] (b) .. controls +(-120:8mm) and +(-90:8mm) .. (Cl) ; \draw (Al) node[above] {\fdelm}; } Wieder die Alternative:
\chemfig{ R-[:30]( =[:90]O ) (-[:160,.25,,,draw=none]\fdelp) -[@{b}:-30,,,,dotted]@{Cl}Cl -[:30,,,,dotted]\chemabove{Al}{\fdelm}Cl_3 } \chemmove{ \draw[elmove] (b) .. controls +(-120:8mm) and +(-90:8mm) .. (Cl) ; } Und schließlich ist hier der Schritt mit Substanzen 4 und 5:
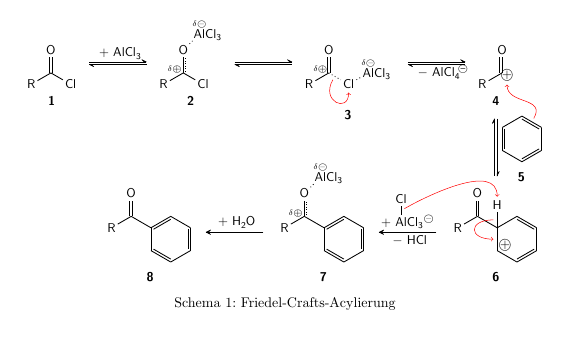
\schemestart \chemfig{R-[:30](-[:-30,.25,,,draw=none]@{fp}\fplus)=^[:90]O} \arrow{<=>[*{0}\chemfig{*6(-=-=[@{b}]-=)}]}[-90,2] \schemestop \chemmove{ \draw[elmove] (b) .. controls +(60:8mm) and +(-90:8mm) .. (fp) ; } In einem kompletten Schema sollte man aufpassen, dass man Bindungen und Atomen mit Edit: Weil mir ein bisschen langweilig war und es mir ja eigentlich Spaß macht, habe ich nun doch versucht, das Schema möglichst originalgetreu umzusetzen. Da das aber nicht mehr die eigentliche Antwort ist, steht der Code mehr oder weniger unkommentiert da. Nur zwei Bemerkungen: zum Nummerieren der Substanzen habe ich
\documentclass{scrartcl} \DeclareNewTOC[ type=scheme, types=schemes,% used in the \listof.. command float, name=Schema, listname={Verzeichnis der Schemata} ]{los} \usepackage{chemfig} \usetikzlibrary{decorations}% chemfig lädt TikZ % eine delokalisierte Doppelbindung \makeatletter \pgfdeclaredecoration{ddbond}{initial}{ \state{initial}[width=2pt]{ \pgfpathlineto{\pgfpoint{2pt}{0pt}} \pgfpathmoveto{\pgfpoint{1pt}{\CF@double@sep}} \pgfpathlineto{\pgfpoint{1.5pt}{\CF@double@sep}} \pgfpathmoveto{\pgfpoint{2pt}{0pt}} } \state{final}{\pgfpathlineto{\pgfpointdecoratedpathlast}} } \makeatother \tikzset{ lddbond/.style={decorate,decoration=ddbond}, rddbond/.style={decorate,decoration={ddbond,mirror}}, elmove/.style={->,red,shorten >=3pt, shorten <=3pt} } \setatomsep{1.78500 em} \setbondstyle{line width = 0.06642 em} \renewcommand*\printatom[1]{\ensuremath{\mathsf{#1}}} \usepackage{chemmacros}% für formale Ladungen \chemsetup{ chemformula/format = \sffamily } \usepackage{chemnum} \begin{document} \begin{scheme} \small\centering \setcompoundsep{6.5em} \setchemnum{format=\bfseries\sffamily} \schemestart \chemname{\chemfig{R-[:30](=[:90]O)-[:-30]Cl}}{\cmpd{chlorid}} \arrow(.base east--.base west){<=>[\ch{+ AlCl3}][][20pt]} \chemname{% \chemfig{ R-[:30]( -[:90,,,,rddbond]O -[:45,,,,dotted]\chemabove{Al}{\fdelm}Cl_3 )(-[:160,.4,,,draw=none]\fdelp) -[:-30]Cl }% }{\cmpd{chlorid-AlCl3-A}} \arrow(.base east--.base west){<=>[][][20pt]} \chemname[4ex]{% \chemfig{ R-[:30]( =[:90]O ) (-[:160,.4,,,draw=none]\fdelp) -[@{b}:-30,,,,dotted]@{Cl}Cl -[:30,,,,dotted]\chemabove{Al}{\fdelm}Cl_3 }% }{\cmpd{chlorid-AlCl3-B}} \chemmove{ \draw[elmove] (b) .. controls +(-120:8mm) and +(-90:8mm) .. (Cl) ; } \arrow(.base east--.base west){<=>[][{\ch[circled]{- AlCl4-}}][20pt]} \chemname {\chemfig{R-[:30](-[:-30,.25,,,draw=none]@{fp}\fplus)=^[:90]O}} {\cmpd{carbonyl-kation}} \arrow{<=>[*{0}\chemname{\chemfig{*6(-=-=[@{b}]-=)}}{\cmpd{benzol}}]}[-90] \chemmove{ \draw[elmove] (b) .. controls +(60:8mm) and +(-90:8mm) .. (fp) ; } \chemname{% \chemfig{ R-[:30](=[:90]O)-[:-30](-[@{b1}:90]@{H}H) *6(-[@{b2}](-[::120,.4,,,draw=none]\fplus)-=-=-) }% }{\cmpd{wheland-komplex}} \chemmove{ \draw[elmove] (b1) .. controls +(180:8mm) and +(180:8mm) .. (b2) ; } \arrow(.base west--.base east)% {->[+ \chemfig{AlCl_3|^{\fminus}-[@{b3}:90]Cl}][\ch{- HCl}]}[180] \chemmove{ \draw[elmove] (b3) .. controls +(30:8mm) and +(90:12mm) .. (H) ; } \chemname{% \chemfig{ R-[:30]( -[:90,,,,rddbond]O -[:45,,,,dotted]\chemabove{Al}{\fdelm}Cl_3 ) (-[:160,.4,,,draw=none]\fdelp) -[:-30]*6(-=-=-=) }% }{\cmpd{acyl-AlCl3}} \arrow(.base west--.base east){->[\ch{+ H2O}]}[180] \chemname{% \chemfig{ R-[:30](=[:90]O) -[:-30]*6(-=-=-=) }% }{\cmpd{acyl}} \schemestop \caption{Friedel-Crafts-Acylierung} \end{scheme} \end{document} Vielen Dank! Jetzt kann ich den Rest des Schemas selbst in LaTeX machen. Du hast meine Probleme genau erkannt. Nochmals vielen Dank!
(24 Mai '14, 21:12)
goldsonne23
+50! Sehr gute und ausführliche Antwort.
(26 Mai '14, 09:14)
Henri
Vielen vielen Dank! Das ist sehr sehr nett von dir! Außerdem ist dies auch eine wunderbare Vorlage für meine kommende Projekte (denn hier ist ja fast alles mit chemfig verarbeit was es gibt). Vielen Dank, jetzt werde ich bestimmt um einiges besser in LaTeX in Punkto Chemie :-)
(13 Jun '14, 04:02)
goldsonne23
Sehr hilfreich! Als Neuling wurde mir dank dir einiges klarer DANKE!
(20 Jul '14, 00:09)
Delsey
1
Weiß vielleicht jemand weshalb das Beispiel bei mir nicht läuft? Es werden Fehlermeldungen bei \setatomsep angegeben
(16 Apr '20, 20:35)
paui
Ergebnis 5 von 7
show 2 more comments
|

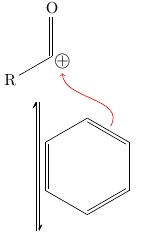
Da bist Du hier nicht ganz verkehrt, da u.a. der chemfig-Autor hier zugegen ist, und sicher Rat zu geben weiß. Evtl. solltest Du den Code Deines bisherigen Ergebnisses ergänzen, so daß sich das rasch weiterbearbeiten läßt.
@cis Nein, der
chemfig-Autor ist nicht zugegen. Das wäre Christian Tellechea. :)